目录
![]()
![]()
![]() 译自《Implementing a Principal Component Analysis (PCA)– in Python, step by step》,一步步地实现了PCA,验证了散布矩阵和协方差矩阵可以得到同样的子空间,并友好地可视化出来,读完后对Python的爱又加深了一层。
译自《Implementing a Principal Component Analysis (PCA)– in Python, step by step》,一步步地实现了PCA,验证了散布矩阵和协方差矩阵可以得到同样的子空间,并友好地可视化出来,读完后对Python的爱又加深了一层。
简介
PCA的主要目的是发现数据中的模式,并利用这些模式在尽量不损失信息的情况下降低数据的维度。
主成分分析vs多重判别分析
多重判别分析MDA和主成分分析PCA都是互相紧密联系的线性变换方法。在PCA中,我们希望找到一些方向(成分)使得数据集的方差最大。在MDA中,我们还需要考虑数据点的类别,让数据最大程度上变得可分,而PCA则完全忽略类别。
换句话说,在PCA中我们将数据集映射到一个子空间中;在MDA中,我们尝试找到一个子空间来区分不同的类别。或者说,在PCA中我们想找到新的坐标系,使得数据的投影尽量长,而在MDA中还需额外考虑不同类别的差异性。
在典型的模式识别问题中,通常先运行MDA后运行PCA。
什么是“好的”子空间
假设我们想把d维的数据映射到k维的子空间(k<d),我们如何选择k,如何判断某个子空间可以“很好地”表示我们的数据呢?
之后,我们将会计算特征向量(成分)然后将其放到一个所谓的“散布矩阵”中。每个特征向量都有一个特征值,告诉我们数据集在该方向投影的长度。如果我们发现所有的特征值大小都非常相似,那么这就说明这个子空间很好。如果有些特征值比另一些大很多,那说明它们含有很多信息。相反,那些特征值接近0的向量则没有多少信息,可以去掉这一维度。
推导PCA
参考斯坦福大学cs229的讲义,我们想找到一个单位向量u,对于给定的点x,其在u方向的投影是![]() ,代表子空间中的一个点,我们希望所有点到原点的距离之和最远(假设我们将数据集的均值处理为0,则这等效于方差最大),也就是说我们想要找到一个单位向量u,使得:
,代表子空间中的一个点,我们希望所有点到原点的距离之和最远(假设我们将数据集的均值处理为0,则这等效于方差最大),也就是说我们想要找到一个单位向量u,使得:
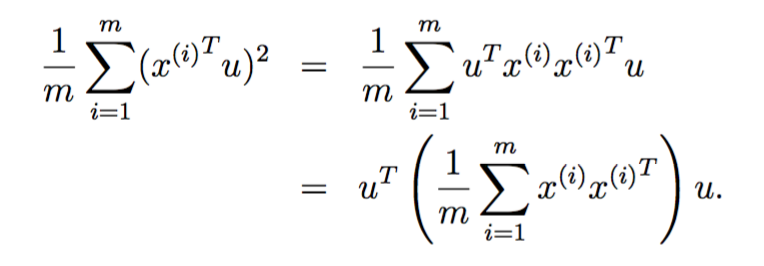
最大化。由于是单位向量,所以我们有约束条件![]() ,这个最大化问题的解是如下矩阵的特征向量:
,这个最大化问题的解是如下矩阵的特征向量:
![]()
这个解是如何得到的呢?可以参考stdcoutzyx的推导:
引入拉格朗日方程
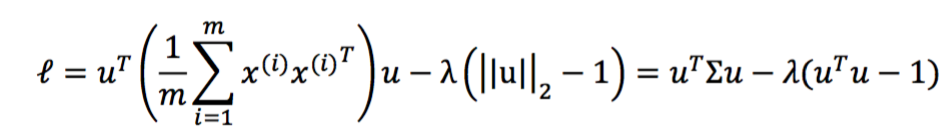
对u求导
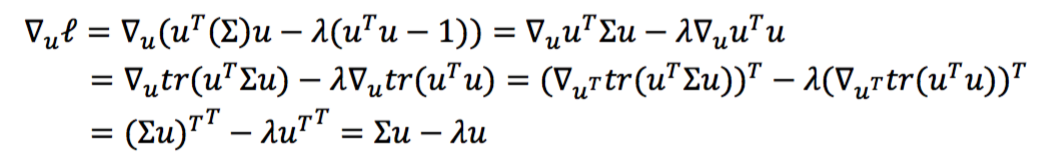
令导数为0,恰好发现u就是Σ的特征向量。
由于Σ是实对称矩阵,所以n*n的Σ矩阵一定有n个正交的特征向量。
在降维的时候,顺序选取特征值最大的k个特征向量,做如下变换即可:
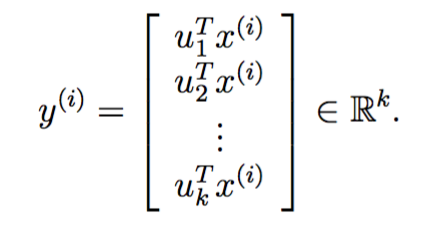
PCA过程
有了上述理论依据,PCA过程可分为6步:
-
将数据集的标签去掉,仅保留d维特征
-
计算d维均值向量(每个维度上的均值构成)
-
计算散布矩阵
-
计算特征向量及其特征值
-
选取特征值最大的k个特征向量,构成d*k的矩阵W
-
对每个数据点,执行如下降维变换:
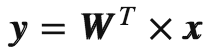
生成一些三维数据
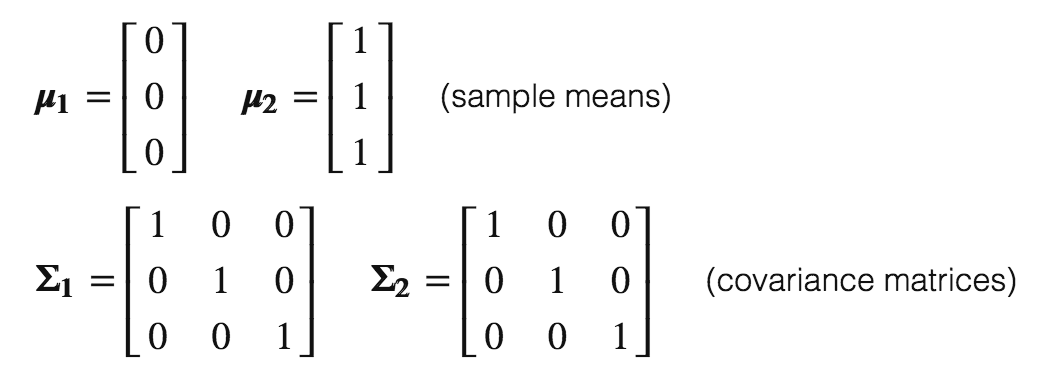
利用2个多元高斯分布生成40个3三维数据点,这两个高斯分布的均值和协方差矩阵分别为:
为什么用三维数据
三维数据可以可视化,降维到二维依然可以,这就是原因。
数据的生成代码如下:
# -*- coding:utf-8 -*- # Filename: main.py # Author:hankcs # Date: 2016-11-09 PM5:18 import numpy as np np.random.seed(234234782384239784) # random seed for consistency, you can remove this if needed mu_vec1 = np.array([0,0,0]) cov_mat1 = np.array([[1,0,0],[0,1,0],[0,0,1]]) class1_sample = np.random.multivariate_normal(mu_vec1, cov_mat1, 20).T assert class1_sample.shape == (3,20), "The matrix has not the dimensions 3x20" mu_vec2 = np.array([1,1,1]) cov_mat2 = np.array([[1,0,0],[0,1,0],[0,0,1]]) class2_sample = np.random.multivariate_normal(mu_vec2, cov_mat2, 20).T assert class1_sample.shape == (3,20), "The matrix has not the dimensions 3x20"
通过上述代码,我们生成了两个3*20的数据集,每个数据点都是三维列向量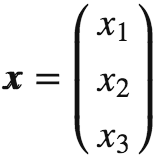 ,数据集则是一个大矩阵
,数据集则是一个大矩阵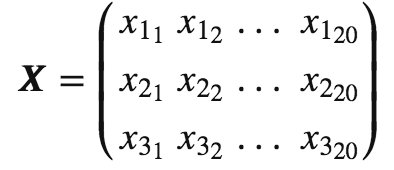 。
。
可视化代码如下:
from matplotlib import pyplot as plt
from mpl_toolkits.mplot3d import Axes3D
from mpl_toolkits.mplot3d import proj3d
fig = plt.figure(figsize=(8,8))
ax = fig.add_subplot(111, projection='3d')
plt.rcParams['legend.fontsize'] = 10
ax.plot(class1_sample[0,:], class1_sample[1,:], class1_sample[2,:], 'o', markersize=8, color='blue', alpha=0.5, label='class1')
ax.plot(class2_sample[0,:], class2_sample[1,:], class2_sample[2,:], '^', markersize=8, alpha=0.5, color='red', label='class2')
plt.title('Samples for class 1 and class 2')
ax.legend(loc='upper right')
plt.show()
得到:
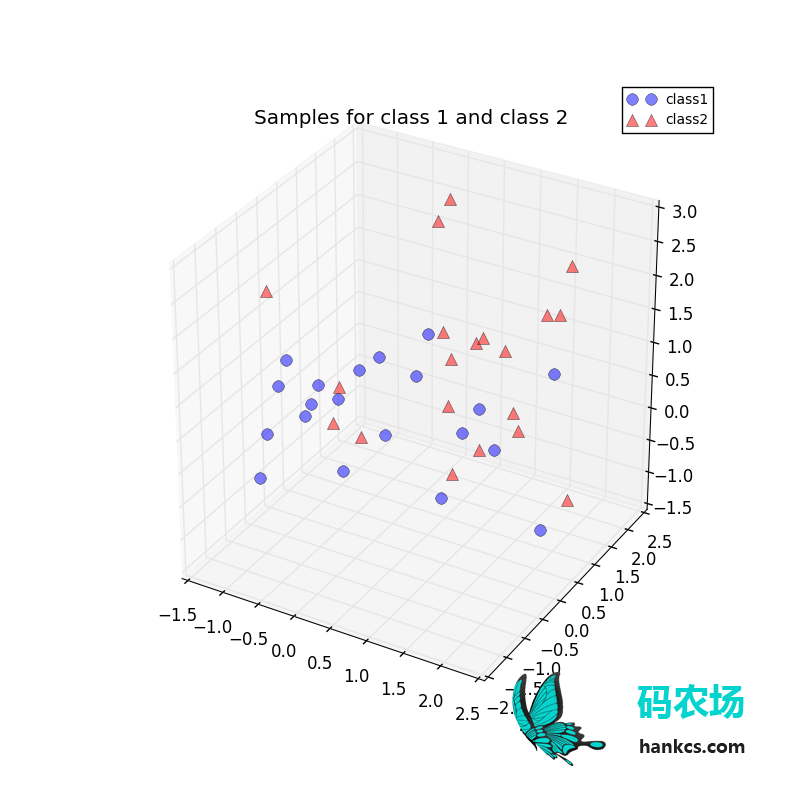
去掉类别
忽略数据集的类别:
all_samples = np.concatenate((class1_sample, class2_sample), axis=1)assert all_samples.shape == (3,40), "The matrix has not the dimensions 3x40"
计算d维均值矩阵
mean_x = np.mean(all_samples[0,:])
mean_y = np.mean(all_samples[1,:])
mean_z = np.mean(all_samples[2,:])
mean_vector = np.array([[mean_x],[mean_y],[mean_z]])
print('Mean Vector:\n', mean_vector)
得到
('Mean Vector:\n', array([[ 0.50576644],
[ 0.30186591],
[ 0.76459177]]))
计算散布矩阵
散布矩阵定义如下:
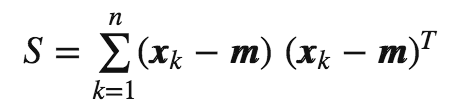
其中,m是均值向量
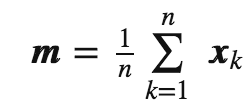
实现如下:
scatter_matrix = np.zeros((3,3))
for i in range(all_samples.shape[1]):
scatter_matrix += (all_samples[:,i].reshape(3,1) - mean_vector).dot((all_samples[:,i].reshape(3,1) - mean_vector).T)
print('Scatter Matrix:\n', scatter_matrix)
得到
('Scatter Matrix:\n', array([[ 48.91593255, 7.11744916, 7.20810281],
[ 7.11744916, 37.92902984, 2.7370493 ],
[ 7.20810281, 2.7370493 , 35.6363759 ]]))
计算协方差矩阵
作为散布矩阵的替代品,也可以利用numpy内置的cov直接计算协方差矩阵。协方差矩阵和散布矩阵的公式非常像,只不过协方差矩阵是散布矩阵的1/(N-1)倍,N代表样本总数。但是无论如何,它们的特征空间是一样的(特征向量相同,只不过特征值被缩放了一个常量倍数)。
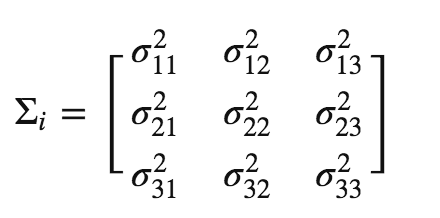
实现如下
cov_mat = np.cov([all_samples[0,:],all_samples[1,:],all_samples[2,:]])
print('Covariance Matrix:\n', cov_mat)
得到
('Covariance Matrix:\n', array([[ 1.25425468, 0.1824987 , 0.18482315],
[ 0.1824987 , 0.97253923, 0.07018075],
[ 0.18482315, 0.07018075, 0.91375323]]))
计算特征向量和对应的特征值
为了验证“对散布矩阵和协方差矩阵而言其特征向量都是相同的”,我们用assert来试验一下,我们还可以将这个常数倍数(40-1=39)算出来:
# eigenvectors and eigenvalues for the from the scatter matrix
eig_val_sc, eig_vec_sc = np.linalg.eig(scatter_matrix)
# eigenvectors and eigenvalues for the from the covariance matrix
eig_val_cov, eig_vec_cov = np.linalg.eig(cov_mat)
for i in range(len(eig_val_sc)):
eigvec_sc = eig_vec_sc[:,i].reshape(1,3).T
eigvec_cov = eig_vec_cov[:,i].reshape(1,3).T
assert eigvec_sc.all() == eigvec_cov.all(), 'Eigenvectors are not identical'
print('Eigenvector {}: \n{}'.format(i+1, eigvec_sc))
print('Eigenvalue {} from scatter matrix: {}'.format(i+1, eig_val_sc[i]))
print('Eigenvalue {} from covariance matrix: {}'.format(i+1, eig_val_cov[i]))
print('Scaling factor: ', eig_val_sc[i]/eig_val_cov[i])
print(40 * '-')
输出:
Eigenvector 1:
[[-0.84190486]
[-0.39978877]
[-0.36244329]]
Eigenvalue 1 from scatter matrix: 55.3988559573
Eigenvalue 1 from covariance matrix: 1.42048348608
('Scaling factor: ', 38.999999999999972)
----------------------------------------
Eigenvector 2:
[[-0.44565232]
[ 0.13637858]
[ 0.88475697]]
Eigenvalue 2 from scatter matrix: 32.4275480129
Eigenvalue 2 from covariance matrix: 0.831475590075
('Scaling factor: ', 38.999999999999986)
----------------------------------------
Eigenvector 3:
[[ 0.30428639]
[-0.90640489]
[ 0.29298458]]
Eigenvalue 3 from scatter matrix: 34.6549343281
Eigenvalue 3 from covariance matrix: 0.888588059694
('Scaling factor: ', 39.0)
----------------------------------------
检查特征向量与特征值
让我们快速验证一下特征向量和特征值的计算是正确的,也就是满足
![]()
这里Σ是协方差矩阵,v是特征向量,lambda是特征值。
实现如下
for i in range(len(eig_val_sc)): eigv = eig_vec_sc[:,i].reshape(1,3).T np.testing.assert_array_almost_equal(scatter_matrix.dot(eigv), eig_val_sc[i] * eigv, decimal=6, err_msg='', verbose=True)
这里numpy的assert_array_almost_equal真是人性化啊,连精度都给考虑了。
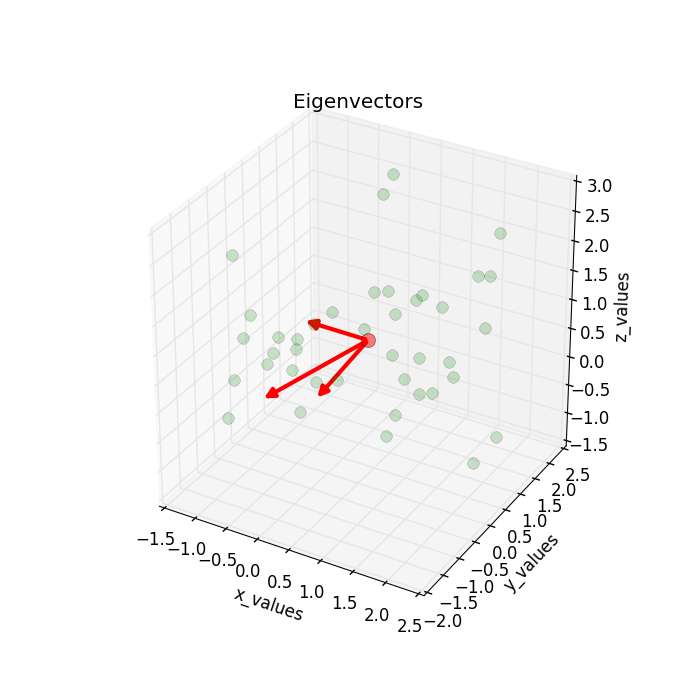
可视化特征向量
在进行下一步之前,不如满足一下我们的好奇心,看看特征向量到底长什么样。
from matplotlib import pyplot as plt
from mpl_toolkits.mplot3d import Axes3D
from mpl_toolkits.mplot3d import proj3d
from matplotlib.patches import FancyArrowPatch
class Arrow3D(FancyArrowPatch):
def __init__(self, xs, ys, zs, *args, **kwargs):
FancyArrowPatch.__init__(self, (0,0), (0,0), *args, **kwargs)
self._verts3d = xs, ys, zs
def draw(self, renderer):
xs3d, ys3d, zs3d = self._verts3d
xs, ys, zs = proj3d.proj_transform(xs3d, ys3d, zs3d, renderer.M)
self.set_positions((xs[0],ys[0]),(xs[1],ys[1]))
FancyArrowPatch.draw(self, renderer)
fig = plt.figure(figsize=(7,7))
ax = fig.add_subplot(111, projection='3d')
ax.plot(all_samples[0,:], all_samples[1,:], all_samples[2,:], 'o', markersize=8, color='green', alpha=0.2)
ax.plot([mean_x], [mean_y], [mean_z], 'o', markersize=10, color='red', alpha=0.5)
for v in eig_vec_sc.T:
a = Arrow3D([mean_x, v[0]], [mean_y, v[1]], [mean_z, v[2]], mutation_scale=20, lw=3, arrowstyle="-|>", color="r")
ax.add_artist(a)
ax.set_xlabel('x_values')
ax.set_ylabel('y_values')
ax.set_zlabel('z_values')
plt.title('Eigenvectors')
plt.show()
得到
排序特征向量
排序前可以先验证一下特征向量的确长度为1:
for ev in eig_vec_sc: np.testing.assert_array_almost_equal(1.0, np.linalg.norm(ev)) # instead of 'assert' because of rounding errors
我们想去掉一个特征值最小的特征维度:
# Make a list of (eigenvalue, eigenvector) tuples eig_pairs = [(np.abs(eig_val_sc[i]), eig_vec_sc[:,i]) for i in range(len(eig_val_sc))] # Sort the (eigenvalue, eigenvector) tuples from high to low eig_pairs.sort(key=lambda x: x[0], reverse=True) # Visually confirm that the list is correctly sorted by decreasing eigenvalues for i in eig_pairs: print(i[0])
得到
55.3988559573 34.6549343281 32.4275480129
没错,就要丢掉那个32了。
选取k个特征值最大的特征向量
三维降低到二维,所以选取前2个特征向量,它们构成3*2的矩阵W:
matrix_w = np.hstack((eig_pairs[0][1].reshape(3,1), eig_pairs[1][1].reshape(3,1)))
print('Matrix W:\n', matrix_w)
得到
Matrix W: [[-0.84190486 0.30428639] [-0.39978877 -0.90640489] [-0.36244329 0.29298458]]
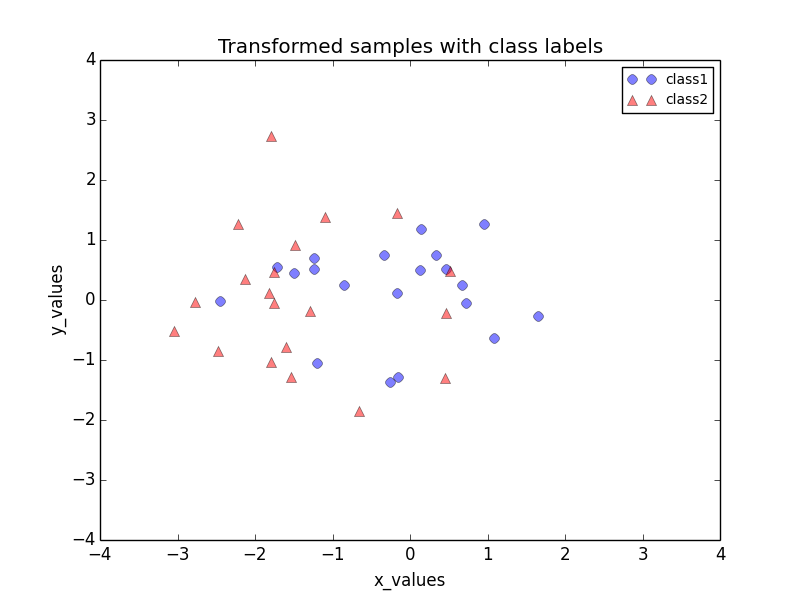
数据变换
利用![]() 将三维数据变换为二维数据:
将三维数据变换为二维数据:
transformed = matrix_w.T.dot(all_samples)
assert transformed.shape == (2,40), "The matrix is not 2x40 dimensional."
plt.plot(transformed[0,0:20], transformed[1,0:20], 'o', markersize=7, color='blue', alpha=0.5, label='class1')
plt.plot(transformed[0,20:40], transformed[1,20:40], '^', markersize=7, color='red', alpha=0.5, label='class2')
plt.xlim([-4,4])
plt.ylim([-4,4])
plt.xlabel('x_values')
plt.ylabel('y_values')
plt.legend()
plt.title('Transformed samples with class labels')
plt.show()
得到
Reference
《Implementing a Principal Component Analysis (PCA)– in Python, step by step》
 码农场
码农场